Par Patrick Pla, Université Paris-Saclay
Niveaux de difficulté : * = embryon; ** = têtard; *** = mature
- EXERCICE 1
- EXERCICE 2
- EXERCICE 3
- EXERCICE 4
- EXERCICE 5
- EXERCICE 6
- EXERCICE 7
- EXERCICE 8
- EXERCICE 9
- EXERCICE 10
- EXERCICE 11
- EXERCICE 12
- EXERCICE 13
- EXERCICE 14
- EXERCICE 15
- REPONSES
EXERCICE 1

**1.1 : D’après vos connaissances, quels sont les rôles respectifs de Dnmt1 et Dnmt3a/3b ?
*1.2 : Décrivez le phénotype des embryons en a). Trouvez des interprétations pour ces résultats.
**1.3 : Qu’est-ce que le bisulfite ? Expliquez le principe de la détection des séquences méthylées sur les cytosines.
*1.4 : Analysez et interprétez les profils de méthylation.
EXERCICE 2
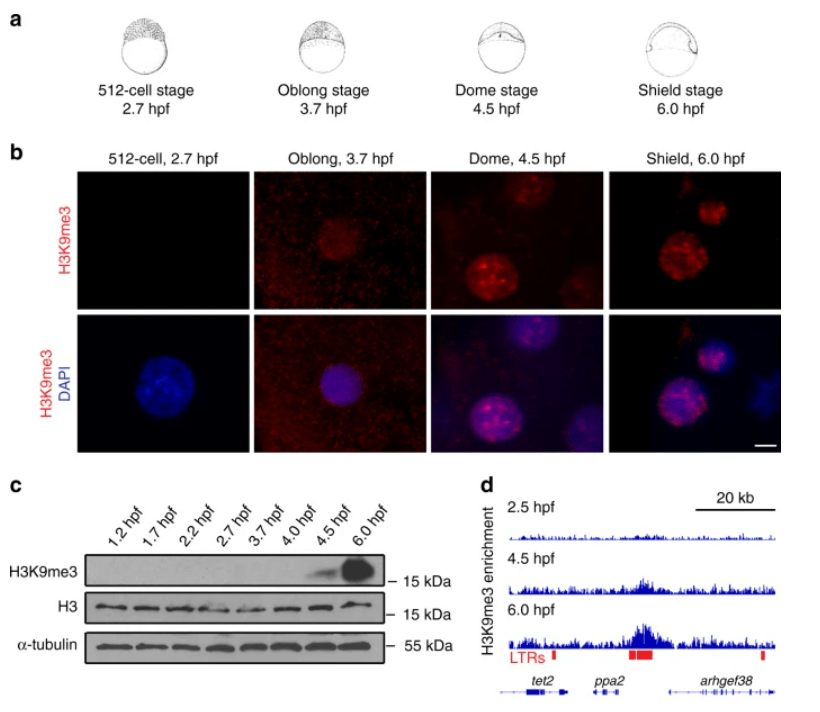
*2.1 : Que veut dire précisément H3K9me3 ?
*2.2 : Analysez les immunofluorescences et interprétez.
*2.3 : Quelles informations supplémentaires nous apporte le western-blot ?
**2.4 : Expliquez le principe du ChIPseq. Analysez les résultats présentés en d.
EXERCICE 3
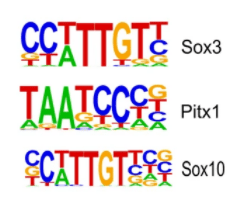
*3.1 : Expliquez comment analyser ces schémas.
*3.2 : Vous cherchez dans le génome des séquences de fixation pour Pitx1 et vous trouvez la séquence TAATCCTG. Qu’en déduisez vous sur la fixation de Pitx1 sur ce site ?
*3.3 : Que remarquez-vous en comparant les sites consensus de Sox3 et de Sox10 ? Interprétez.
EXERCICE 4

*4.1 Quel est l’intérêt de comparer les séquences des deux ascidies ?
*4.2 Que remarquez-vous sur la position des séquences les plus conservées chez les deux ascidies ? Interprétez.
*4.3 Comment révèle-t-on la localisation de l’expression du gène LacZ pour obtenir une image comme en B ?
*4.4 Quel est l’intérêt d’avoir trouvé et indiqué des sites de fixation de facteurs de transcription sur la comparaison de séquence en C ?
*4.5 Que nous révèle la figure D en comparaison avec la figure B ?
*4.6 Analysez et interprétez les résultats en E.
**4.7 Quel est l’intérêt d’étudier la construction -3052/+1 avec la boîte E délétée (F) ?
EXERCICE 5
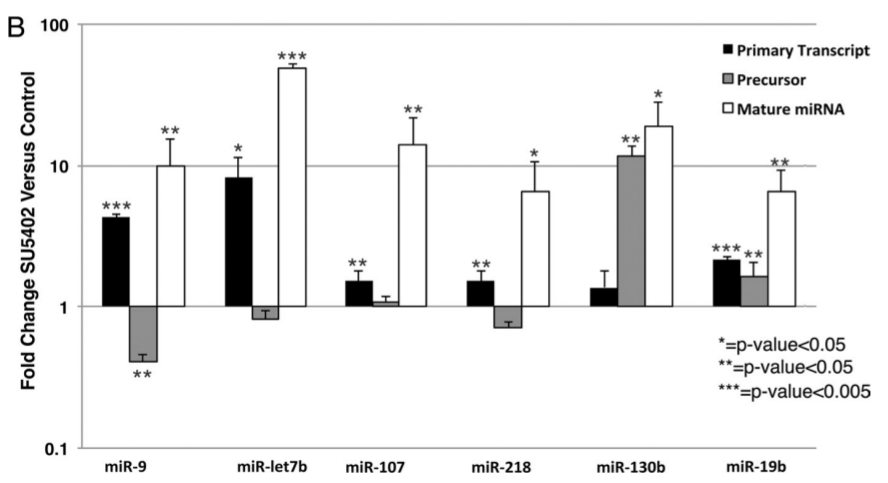
*5.1 Quel est l’ARN polymérase qui synthétise les pri-miARN ?
**5.2 Quels sont les complexes qui permettent de produire les pré-miARN et les ARN matures ? Où ces maturations ont-elles lieu dans la cellule ?
**5.3 Comment faire pour distinguer lors de la PCR suivant la RT les pri-, pré-miARN et les miARN matures ?
*5.4 Analysez et interprétez les résultats de l’expérience.
EXERCICE 6
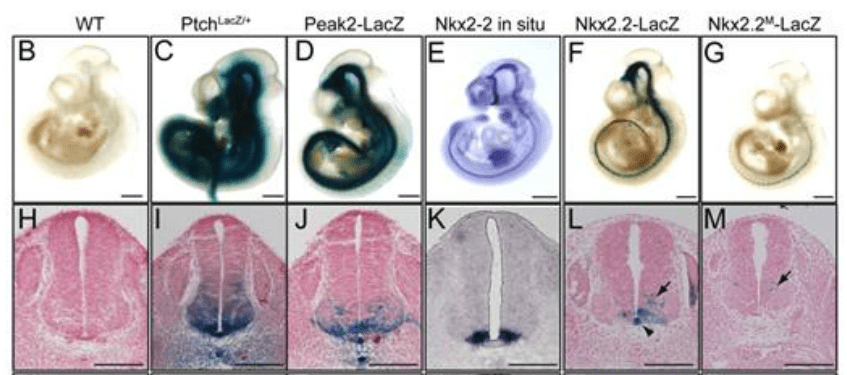
*6.1 Quel est l’intérêt d’étudier un embryon tel que PtchLacZ/+ ?
*6.2 Analysez le résultat de la coloration Xgal en C et I. Quelle est la signification de ce qui est observé par rapport à la fonction de Patched ?
**6.3 Des expériences de ChiPseq ont mis en évidence une séquence Peak2 dans le promoteur de Ptch. Rappelez quel est le principe de cette technique.
*6.4 Analysez et interprétez les résultats obtenus en D, J.
*6.5 Analysez et interprétez les résultats obtenus en F, L.
*6.6 Quelles informations supplémentaires nous apportent les résultats en G, M ?
EXERCICE 7
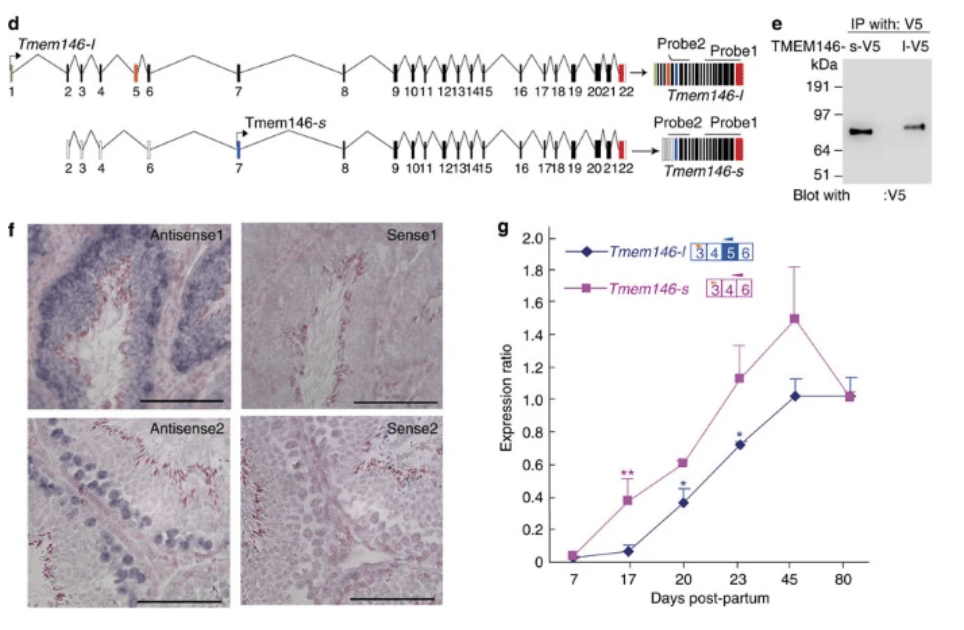
*7.1 Quel est le processus mis en évidence ici ? Justifiez.
*7.2 Pourquoi l’une des formes de la sous-unité du canal est plus courte ?
*7.3 Sur le western-blot en e, pourquoi choisit-on un anticorps qui reconnait la partie C-terminale de la protéine ?
**7.4 Comment choisir les sondes en hybridation in situ pour ne localiser que les ARNm de la forme longue ?
*7.5 A quoi servent les témoins avec les sondes sens ?
*7.6 Que déduisez-vous de l’analyse de la figure f ?
**7.7 Comment a été choisi la région à amplifier par qPCR (regardez et commentez les diagrammes au dessus des courbes en g) ?
*7.8 Commentez les résultats de la RT-qPCR en g.
EXERCICE 8
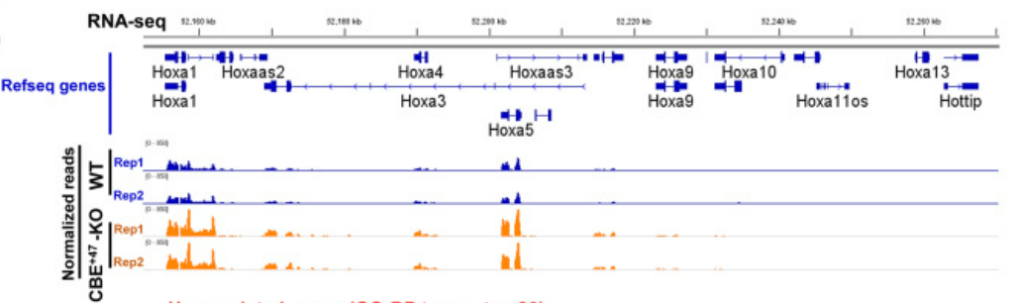
**8.1 Qu’est-ce qu’un TAD ?
**8.2 Analysez les résultats et essayez de trouver une hypothèse pour les expliquer.
EXERCICE 9
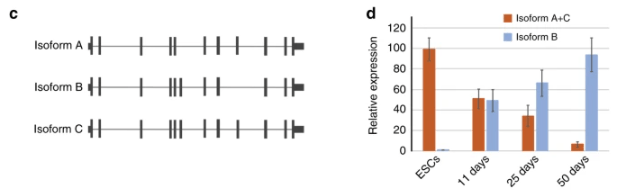
*9.1 Quel phénomène est ici mis en évidence pour expliquer la production des trois isoformes de ZNF507 ?
**9.2 Par RT-qPCR, on souhaite distinguer l’expression des isoformes A et C de l’expression de l’isoforme B. Comment réaliser cet objectif ?
*9.3 Que constate-t-on sur l’expression des isoformes au cours de la différenciation ?
EXERCICE 10
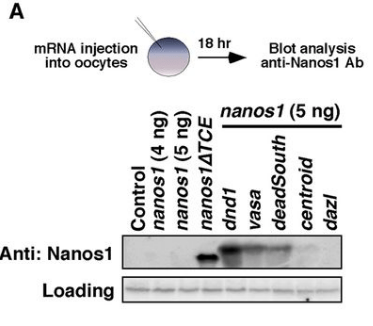
*10.1 : Proposez un mécanisme pour expliquer comment la séquence TCE bloque la traduction de l’ARNm de nanos1.
*10.2 : Analysez et interprétez ces résultats. Pourquoi la bande dans le puits nanos1ΔTCE est-elle plus basse que les autres ?
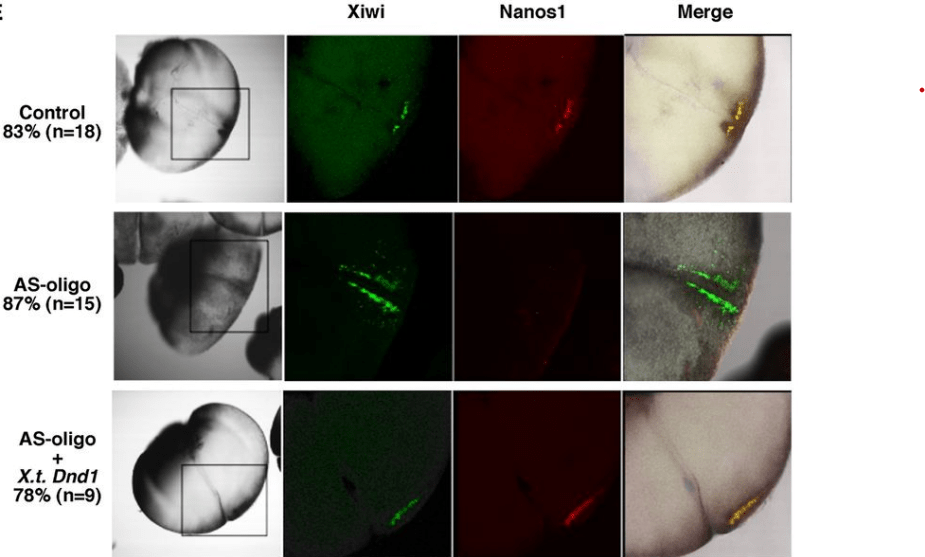
**10.3 : Analysez et interprétez cette expérience.
EXERCICE 11
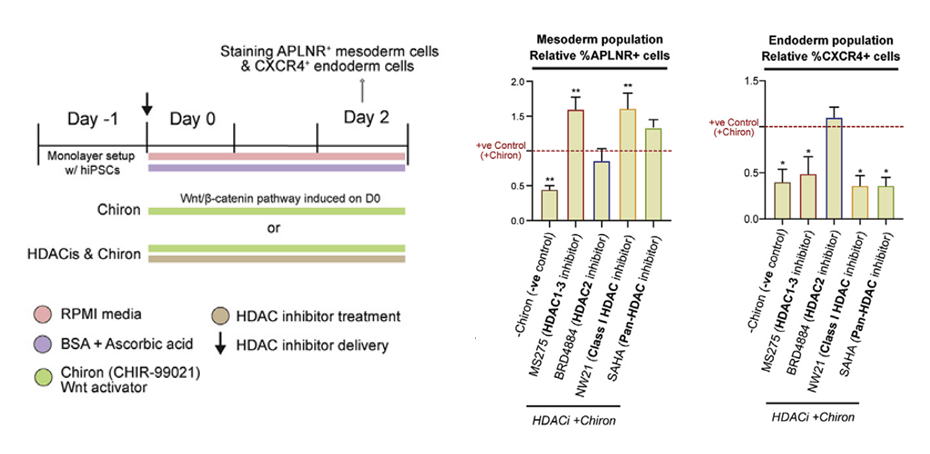
*11.1 : Quel est l’effet du Chiron sur la détermination des cellules en mésoderme et en endoderme ? Interprétez.
*11.2 : Rappelez ce que sont les histones désacétylases.
**11.3 : Analysez l’effet des différents inhibiteurs de HDAC et concluez sur le rôle des HDAC dans la différenciation endomésodermique des cellules iPS.
EXERCICE 12
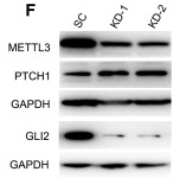
Dans une population de cellules de médulloblastome cultivée in vitro, le gène codant la protéine METTL3 est rendu non fonctionnel par le système CRISPR-Cas9 avec 2 cibles indépendantes dans le gène (KD-1 et KD-2). SC = contrôle où aucun gène n’est ciblé par le système CRISPR-Cas9. On extrait quelques jours plus tard les protéines et on les analyse par western-blot avec des anticorps reconnaissant les protéines indiquées à gauche. GAPDH est une protéine de ménage. Le panel du haut correspond à la membrane où METTL3 et PTCH1 ont été révélés et le panel du bas à la membrane où GLI2 a été révélé. Source : https://www.cell.com/cell-reports/fulltext/S2211-1247(22)01386-9
**12.1 Pourquoi réalise-t-on deux invalidations indépendantes du gène codant METTL3
*12.2 Est-ce que l’invalidation du gène METTL3 a fonctionné ?
*12.3 Analysez et interprétez les résultats concernant l’expression de PTCH1 et de GLI2.
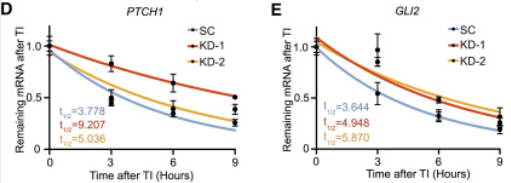
*12.4 Analysez et interprétez ces résultats.
**12.5 Est-ce que ces résultats peuvent expliquer ce que vous avez observé à la question 12.3 ? Emettez des hypothèses.
EXERCICE 13
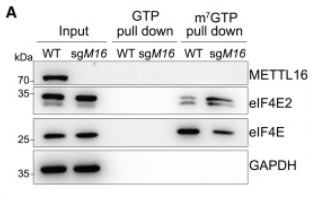
*13.1 Quel est l’intérêt de faire un m7GTP pull-down ?
*13.2 Quel est l’intérêt de réaliser un western-blot de l’input (l’extrait protéique total) ?
*13.3 Analysez les résultats des pull-downs.
*13.4 Sachant que eIF4E2 inhibe l’initiation de la traduction et que eIF4E active l’initiation de la traduction, déduisez le rôle de METTL16 sur la traduction.
EXERCICE 14
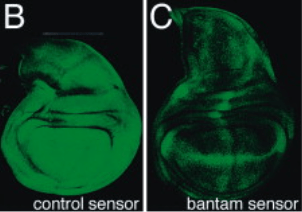
*14.1 Pourquoi utilise-t-on le promoteur de la tubuline ?
*14.2 En analysant l’expression de la GFP dans le disque imaginal de l’aile dans les deux drosophiles transgéniques, que peut-on déduire de l’expression et de l’activité de Bantam ?
EXERCICE 15
Les mutants clueless (clu) de la drosophile présentent une diminution générale de la synthèse de protéines. On cherche à savoir pourquoi.
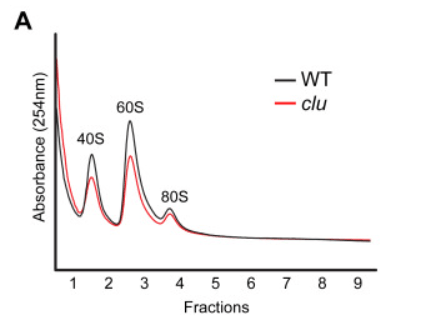
*15.1 A quoi correspondent les fractions ribosomales 40S, 60S et 80S ?
*15.2 Que peut-on déduire de cette expérience ?
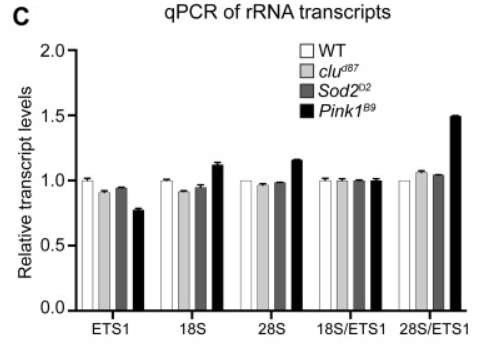
*15.3 Analysez les résultats de cette expérience et conclure.
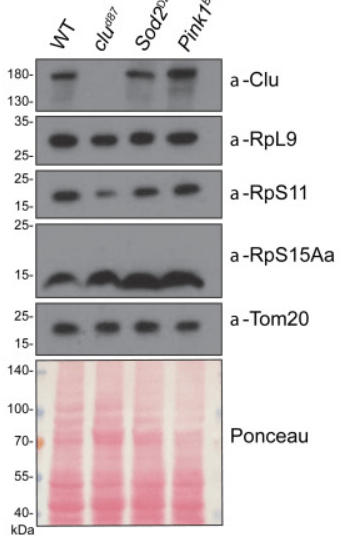
*15.4 Que permet de voir le rouge Ponceau ?
*15.5 Analysez les résultats de l’expérience et concluez.
REPONSES
1.1 : Dnmt1 catalyse la méthylation de maintien des cytosines (après la réplication, méthylation sur les brins néosynthétisés) alors que Dnmt3a/3b est impliqué dans la méthylation des cytosines de novo. 1.2 : Les embryons présentent des malformations sévères et un retard de croissance. Il est difficile de distinguer des structures et des axes précis (surtout pour l’embryon Dnmt1-/-). Dnmt1 et Dnmt3a/3b méthylent les cytosines des séquences CpG et cela a un effet répresseur localisé sur la transcription. Par conséquent, les embryons mutés doivent avoir de multiples gènes transcrits de manière ectopique ou trop précocement ce qui cause une sévère désorganisation. 1.3 : L’ADN génomique est coupé par une ou plusieurs enzymes de restriction. Les fragments sont ensuite traités avec le bisulfite. En présence de ce composé chimique, les cytosines sont converties en uracile, alors que les cytosines méthylées ne sont pas affectées. L’ensemble des fragments traités est ensuite amplifié par PCR puis séquencé. 1.4 : Les profils de méthylation des hétérozygotes sont à peu près normaux et l’absence de Dmt3b peut être compensée par Dnmt3a et inversement. Notons que la compensation de Dnmt3b par Dnmt3a n’est que partielle. L’absence des deux Dnmt3a/b provoque une baisse drastique de la méthylation et également l’absence de Dnmt1.
2.1 : Cela désigne une triméthylation de la lysine en position 9 dans l’histone H3. 2.2 : On voit une fluorescence apparaître progressivement au fil du développement. Cela veut dire qu’il y a de plus en plus de triméthylation de la lysine 9 de l’histone H3. Cela peut vouloir dire qu’il y a de plus en plus d’histone H3 de manière générale ou cela peut vouloir dire qu’il y a de plus en plus de lysines 9 dans la population des histones H3 qui sont triméthylés (et non plus diméthylés ou simplement méthylés ou pas méthylés du tout). 2.3 : La quantité d’histone H3 ne varie pas (à part une légère baisse à 2.7 hpf et 3.7 hpf) si on la compare au contrôle alpha-tubuline. Cela veut donc dire que la forte augmentation de la présence de triméthylation de la lysine 9 observée à 4,5 hpf et 6 hpf est dûe à l’augmentation de la méthylation de lysine et non à une augmentation générale de la quantité d’histone H3. 2.4 : De l’ADN génomique est traité avec un agent fixateur pour que les protéines restent accrochées dessus. L’ADN est fragmenté par sonication puis incubé avec un anticorps reconnaissant une protéine particulière sur l’ADN. Après précipitation, on purifie l’ADN obtenu dans le culot et on le séquence à haut débit. Ici, sur ce fragment de chromatine, on observe au cours du temps une augmentation générale de l’enrichissement qui signe la présence de la triméthylation de la lysine. Une séquence centrale est particulièrement enrichie, signant une triméthylation particulièrement poussée dans cette région du génome.
3.1 : Ces schémas représentent les séquences consensus de fixation de facteurs de transcription sur leurs séquences cibles dans les promoteurs et les enhancers/silencers. Les séquences consensus d’un facteur de transcription donné ne sont jamais à 100% conservés à travers tout le génome. Lorsqu’à une position donnée, il n’y a qu’une seule grande lettre qui prend toute la hauteur (le T en 4ème position pour Sox3 par exemple) cela veut dire que le nucléotide est toujours présent. Lorsqu’il y a plusieurs lettres l’une sur l’autre à une position, la taille relative des lettres indique la probabilité de trouver cette lettre dans la séquence consensus à cette position. Par exemple, en 1ère position pour Sox3 on trouvera très fréquemment un C, moins fréquemment un G ou un T et très rarement un A. 3.2 : C’est un site putatif ou potentiel qui correspond bien à ce qui est attendu d’une séquence où se fixe Pitx1. Mais en aucun cas, cela prouve que Pitx1 se fixe effectivement à cet endroit. Il faut faire des tests spécifiques de fixation de facteurs de transcription (EMSA, ChIPseq…). 3.3 : On trouve une ressemblance, notamment dans la partie centrale. C’est normal puisque Sox3 et Sox10 font partie d’une même famille multigénique et par conséquent, malgré des divergences, les sites de fixation à l’ADN ont conservé des ressemblances et donc aussi les séquences de l’ADN où ces facteurs de transcription s’accrochent.
4.1 : Si des séquences sont plus conservées que d’autres entre les 2 espèces c’est qu’il y a sans doute eu une sélection et que les mutants dans ces séquences ont été éliminées. Par conséquent, ces séquences doivent avoir une importance fonctionnelle. 4.2 : Les séquences les plus conservées se trouvent en premier lieu dans les exons, ce qui est logique puisque la séquence codant les acides aminés de la protéine se trouve dans les exons (mais la séquence codante ne recouvre pas tous les exons (il y a le 5’UTR et le 3’UTR qui sont dans les exons mais qui ne sont pas traduits)). Ensuite, on trouve des séquences très conservées en amont du site de démarrage de la transcription et aussi dans une partie de l’intron. Ces deux dernières séquences pourraient être des séquences régulatrices de la transcription. 4.3 : Les embryons sont fixés (suffisamment pour éviter la dégradation des tissus, mais pas trop pour ne pas inactiver les enzymes). LacZ code la beta-galactosidase qui est une enzyme. On lui présente ses substrats Xgal et le cyanide ferrique (et pas le galactose qui serait son substrat habituel dans une bactérie !) et l’enzyme catalyse une réaction qui donne un produit coloré en bleu. Une post-fixation est parfois nécessaire pour éviter la disparition de la coloration avec le temps. 4.4 : Les sites putatifs de fixation de facteurs de transcription peuvent donner une idée des facteurs qui pourraient être impliqués dans le contrôle de l’expression de FoxF à partir de ces éléments. Trouver que ces séquences particulières sont conservées entre deux espèces donne du poids au fait que ces séquences sont fonctionnelles et importantes. Mais cela ne constitue pas une preuve de la fixation réelle de ces facteurs de transcription sur ces séquences. 4.5 : On voit que ce fragment d’ADN restreint l’expression de LacZ aux cellules TVC alors que le grand fragment -3052 à +1 conduisait aussi LacZ à être exprimé dans l’épiderme. Donc la séquence qui contrôle l’expression dans l’épiderme se trouve en dehors du fragment -1135 à -840. Il reste possible que d’autres séquences contrôlent l’expression dans les TVC en dehors de ce fragment, même s’il parait suffisant, le niveau d’expression n’est peut-être pas optimal. 4.6 : La délétion de la boîte E aboutit à une perte totale de l’expression du gène rapporteur dans les TVC. Elle est donc nécessaire pour que FoxF y soit exprimé. La délétion des éléments Ets individuellement a des conséquences moins sévères mais significatives et la délétion de deux de ces éléments a des conséquences sévères. Cela indique que la délétion d’un élément Ets peut être partiellement compensée par la présence des autres mais pas la délétion de deux éléments. 4.7 : Il s’agit de vérifier s’il n’y a pas un autre élément régulateur dans le grand fragment qui pourrait compenser la perte de la boîte E. Il n’y en a pas. On constate aussi que l’expression dans l’épiderme semble plus forte que dans le contrôle sans la délétion ce qui suggère que la boîte E contenant des éléments de régulation inhibiteurs de l’expression dans l’épiderme.
5.1 : L’ARN polymérase II. 5.2 : Les pré-miARN sont produits par le complexe Drosha dans le noyau et les miARN mature sont produits par Dicer puis RISC dans le cytoplasme. 5.3 : Pour les pri-miARN, il faut choisir au moins une des deux amorces de telle manière à ce qu’elle reconnaisse des séquences qui ne sont présentes que dans le pri-miARN et non pas dans les formes plus matures car elles auront été excisées. Pareil pour les amorces pour les pré-miARN. Pour le miARN, les séquences seront trouvées dans les précurseurs donc on ne peut pas trouver d’amorces spécifiques mais on peut soustraire le signal obtenu par les précurseurs du signal obtenu avec les amorces des miARN. 5.4 : Globalement l’inhibition de la signalisation FGF aboutit à une augmentation des miARN matures. Cela provient en partie d’une stimulation de la transcription des gènes codant ces miARN car on observe une augmentation de la quantité de pri-miARN. Dans certains cas, la baisse de la quantité de pré-miARN indique une stimulation de leur maturation en miARN matures (miR-9 et miR-218 et dans une moindre mesure miR-let7b). Pour d’autres cas, c’est l’étape de maturation des pri- en pré-miARN qui est stimulée (miR-130b). On en conclut que FGF inhibe la production et la maturation des précurseurs des miARN à différents niveaux.
6.1 : Le gène rapporteur LacZ est inséré dans le locus d’un gène d’intérêt et donc sa transcription est soumise aux mêmes séquences régulatrices que ce gène. Cette insertion peut provoquer une perte-de-fonction mais seul un des deux allèles est ainsi muté et en général, l’allèle sauvage restant est capable de compenser et le phénotype de l’embryon est normal ou très peu altéré. Dans ce cas précis, Ptch code le récepteur de Shh donc on peut savoir où ce récepteur est exprimé. 6.2 : LacZ est exprimé le long de l’embryon dans un bon tiers ventral du tube neural avec un gradient (diminution an allant vers la région dorsale). Il est exprimé dans la corde et un peu dans le mésenchyme latéral adjacent, sans doute le sclérotome qui va former les vertèbres. Comme LacZ est sous le contrôle des séquences régulatrices de Patched, on peut en déduire que le récepteur de Shh est probablement exprimé dans les mêmes régions et cela donne une idée où le morphogène Shh peut agir (il est produit par la corde et la plaque du plancher (la partie la plus ventrale du tube neural)). 6.3 : voir cette page . 6.4 : Le gène rapporteur est exprimé dans une partie seulement du domaine d’expression de Ptch qui a été observé en C, I. Il manque notamment l’expression dans le sclérotome et dans la partie la plus dorsale du domaine d’expression dans le tube neural. D’autres éléments régulateurs que Peak2 doivent intervenir pour contrôler la transcription de Ptch. 6.5 : On observe une expression irrégulière du gène rapporteur dans la partie ventrale du tube neural, d’un côté en grande majorité (à droite sur l’image, gauche ou droite pour l’embryon on ne peut pas le savoir). Quand on compare avec l’hybridation in situ en E, K, on constate que la séquence régulatrice utilisée ne permet pas de bien récapituler l’expression du gène Nkx2-2. Il y a même une expression ectopique (soulignée par les flèches) hors du domaine habituel d’expression de Nkx2-2 ce qui indique que d’autres séquences régulatrices de ce gène doivent être répressives. 6.6 L’expression du gène rapporteur disparait presque complètement ce qui nous indique que les séquences régulatrices mutées sont importantes et que Gli1 est très probablement impliqué. Une petite partie de l’expression ectopique est maintenue (flèche) ce qui indique que le contrôle de cette partie du patron d’expression n’est pas réalisé par Gli1 mais par un autre facteur de transcription qui peut toujours se fixer sur la séquence régulatrice malgré la mutation introduite.
7.1 : On observe que les transcrits finaux n’ont pas la même composition en exons avec l’exon 1 et l’exon 5 manquant dans l’un des cas. Comme le montre le western-blot en e, cela donne des protéines de taille différente. On en déduit qu’il s’agit d’un cas d’épissage alternatif. 7.2 : Le site de démarrage de la traduction de la forme longue est dans l’exon 1. Or celui-ci est épissé dans l’ARNm de la forme courte et ce n’est que dans l’exon 7 que se trouve l’AUG de démarrage de la traduction. La protéine est donc plus courte car il lui manque les acides aminés codés par les exons 1 à 6. 7.3 : La partie N-terminale de la protéine est différente chez la forme longue et courte et donc il faut prendre un anticorps qui reconnait une partie commune entre les deux formes de la protéine et c’est le cas de la partie N-terminale. 7.4 : On doit choisir des séquences d’ARNm anti-sens qui s’hybrident avec des séquences spécifiques de la forme longue. La forme longue peut être reconnue par une sonde qui s’hybride avec les séquences correspondantes à l’exon 1 ou à l’exon 5. 7.5 : Les hybridations avec les sondes sens servent de témoin négatif : elles permettent d’estimer le marquage de bruit de fond lié à la procédure. 7.6 : Avec la sonde antisense 1, on voit que l’une ou l’autre des formes est exprimée dans toute la paroi des tubes séminifères alors que la sonde antisens 2 qui ne reconnait que la forme longue donne un signal que dans des cellules du côté basal des tubes séminifères dans la région où se trouvent les spermatogonies. On peut penser que la forme longue est d’abord exprimée dans les spermatogonies et qu’ensuite c’est uniquement la forme courte qui est exprimée dans des cellules germinales plus matures. Notez que la forme courte peut aussi être exprimée dans les spermatogonies (on n’a aucun moyen de le prouver ou de l’infirmer avec les données présentées). 7.7 : Le fragment à amplifier spécifique de la forme longue correspond à l’exon 5. Le fragment à amplifier pour la forme courte est à cheval entre l’exon 4 et l’exon 6. Les oligonucléotides utilisés pour amplifier ce deuxième fragment peuvent reconnaitre des séquences correspondantes aux formes longues mais le transcrit sera de taille plus importante dans ce cas, ce qui permettra de distinguer les transcrits. 7.8 : La forme courte est exprimée plus précocément que la forme longue et est exprimée plus fortement même lorsque la forme longue est également produite à partir des jours 17-20 après la naissance. A 80 jours après la naissance, les quantités relatives s’égalisent cependant par baisse de la quantité d’ARNm de la forme courte.
8.1 : C’est une région de la chromatine (flanquée par des isolateurs où se fixent CTCF) où les interactions entre séquences régulatrices de la transcription sont privilégiées. 8.2 : On constate que le nombre de séquences lues en RNAseq et donc le niveau de transcription est globalement augmenté pour tous les gènes du complexe entre Hoxa1 et Hoxa9. La transcription des gènes plus en 5′ dans le complexe reste éteinte. La frontière de TAD qui a été ôtée chez le mutant est en 3′ du complexe donc du côté des gènes dont la transcription a été stimulée. On peut penser que leur transcription chez le mutant est tombée sous l’influence d’un enhancer qui se trouve habituellement dans un autre TAD et qui n’agit pas sur eux dans les cellules sauvages.
9.1 : On observe que certains exons sont présents dans des isoformes et pas dans d’autres (par exemple, le 6ème exon est présent dans les isoformes B et C mais pas dans l’isoforme A). On en déduit qu’il s’agit d’un épissage alternatif. 9.2 : Les isoformes A et C ont l’exon 9 en commun mais il n’est pas présent dans l’isoforme B. Il suffit donc de choisir des amorces pour la qPCR qui soient dans l’exon 9. Pour suivre l’expression de l’isoforme B qui n’a pas d’exon 9, on peut choisir des amorces dans les exons 8 et 10, la taille du fragment obtenu sera plus courte pour l’isoforme B que pour les isoformes A et C (où l’exon 9 rallonge la séquence entre les deux amorces). 9.3 : L’expression des isoformes A et C sont quasi-exclusives dans les cellules ES non différenciées mais elle diminue au cours de la différenciation neuronale. Dès le 11ème jour, l’épissage alternatif qui aboutit à l’expression de l’isoforme B est activé et représente la moitié des transcrits. La proportion de transcrits de l’isoforme B augmente ensuite jusqu’à atteindre plus de 90% en fin de protocole. On comprend que ZNF507 a des fonctions différentes dans les cellules souches et dans les cellules différenciées : ce n’est plus tout à fait la même protéine.
10.1 : La structure secondaire de l’ARNm de nanos1 provoquée par la séquence TCE juste en arrière du codon d’initiation pourrait empêcher la progression des ribosomes. 10.2 : En absence de TCE, l’ARNm de nanos1 est bien traduit en protéine mais celle-ci est plus courte que la protéine normale car il manque la séquence correspondante au TCE (qui est en 3′ de l’AUG d’initiation donc dans la séquence codante traduite). En présence de dnd1, vasa et deadSouth, on détecte la protéine Nanos1 montrant que ces protéines sont nécessaires pour permettre la traduction des ARNm de nanos1 qui possèdent leur TCE. Il y a un très léger effet aussi en présence de centroid. 10.3 : Dans les embryons contrôle, on observe une co-localisation entre Xiwi et Nanos1 indiquant que Nanos1 est localisée dans le plasme germinal. En absence de Dnd1, le plasme germinal est toujours présent (mais différemment localisé) comme l’atteste l’expression de Xiwi mais on ne détecte plus Dnd1. Le sauvetage de ces embryons par une protéine Dnd1 restaure partiellement la bonne localisation du plasme germinal. On déduit de ces expériences que Dnd1 est nécessaire pour la production de la protéine Nanos1 et que celle-ci est nécessaire à la bonne localisation du plasme germinal.
11.1 : Sans Chiron (première barre à gauche des graphes), il y a moitié moins environ de cellules qui expriment un marqueur mésodermique et endodermique. On en déduit que la voie canonique Wnt/beta-caténine stimule la détermination en mésoderme et en endoderme. Parmi les cibles de beta-caténine/TCF, il doit y avoir des gènes importants pour l’engagement vers l’un et/ou l’autre feuillet. 11.2 : Ce sont des enzymes qui catalysent la perte du groupe acétyl sur les lysines de la queue N-terminale des histones et ce qui renforce les liaisons faibles entre les histones et l’ADN et inhibe la transcription en diminuant l’accessibilité des facteurs de transcription à leur séquence cible. 11.3 : L’inhibition de tous les HDAC ou des HDAC1-3 aboutit à une augmentation de la détermination en mésoderme au détriment de la détermination en endoderme. Cependant, l’inhibition sélective de HDAC2 n’a pas d’effet significatif. On en déduit que c’était l’inhibition de HDAC1 et de HDAC3 qui a véritablement influencé le changement de détermination. Donc les désacétylations d’histones par HDAC1 et HDAC3 (et donc des inhibitions de l’expression de gènes contrôlées par les séquences dont l’état de condensation de la chromatine a été modifiée par ces 2 enzymes) sont nécessaires pour une détermination maximale en endoderme et pour inhiber la détermination en mésoderme.
12.1 : Il s’agit de vérifier la spécificité de l’action de CRISPR-Cas9 et de voir si on obtient le même phénotype avec deux cibles indépendantes sur le même gène. Si ce n’est pas le cas, ça veut dire qu’il y a eu dans un des cas une édition du génome ailleurs que dans METTL3, ce qui a pu influencer le phénotype. 12.2 : La protéine de ménage GAPDH est à peu près pareillement exprimée dans le cas SC et KD-2 et moins dans KD-1 ce qui rend les conclusions moins faciles pour KD-1. Néanmoins, on observe une nette diminution de l’expression de METTL3 par l’action de CRISPR-Cas9 dans les deux cas où le gène est ciblé. Cependant, un peu de METTL3 est toujours présent : soit CRISPR-Cas9 n’a pas pu agir correctement dans toutes les cellules de la population dont on a extrait les protéines, soit il s’agit du METTL3 produit avant l’action de CRISPR-Cas9 et qui n’a pas encore été entièrement dégradé. 12.3 : L’expression de la protéine PTCH1 augmente lorsque la quantité de METTL3 est diminuée tandis que c’est l’inverse pour GLI2. METTL3 inhibe donc l’expression de PTCH1 (soit au niveau de la transcription, soit au niveau de la traduction) et METTL3 active l’expression de GLI2 (là aussi au niveau de la transcription ou de la traduction). Alternativement, METTL3 peut influencer la stabilité de ces protéines. 12.4 : L’inhibition de la transcription permet de suivre la survie des ARNm qui ont été produits avant. Pour les ARNm de PTCH1 on constate que la diminution de l’expression de METTL3 a plutôt un effet stabilisant (avec un effet plus fort de KD-1 relativement à KD-2). On observe la même chose avec les ARNm de GLI2 avec cette fois-ci un effet similaire entre KD-1 et KD-2. On en déduit que METTL3 a un effet déstabilisant sur les ARNm de ces deux gènes, stimulant sans doute leur dégradation. 12.5 : La stabilisation des ARNm de PTCH1 lorsque METTL3 est moins présent peut expliquer l’augmentation de la quantité de protéine PTCH1 observé en western-blot (cependant on ne retrouve pas l’effet différentiel de KD-1 et de KD-2 sur le western-blot). En revanche, pour GLI2 la stabilisation des ARNm va à l’encontre de la chute importante de la quantité de protéine. D’autres mécanismes que la stabilisation des ARNm doivent être à l’oeuvre au niveau transcriptionnel ou traductionnel.
13.1 : La coiffe des ARNm se compose d’une guanosine méthylée en position N7 donc il s’agit de séparer les protéines qui se fixent à cette coiffe des autres protéines. 13.2 : Cela permet d’abord de vérifier que la protéine METTL16 est bien absente dans les cellules sgM16 alors qu’elle est présente dans les cellules WT. Ensuite, cela permet de vérifier que les quantités de protéines sont similaires entre les 2 conditions, GAPDH qui est étudié comme un contrôle mais aussi eIF4E2 et eIF4E. Toutes différences dans les pull-downs sera lié à un accrochage différentiel avec la coiffe. 13.3 : Il n’y a rien dans le pull-down GTP, ce qui indique que ce qui est récupéré par le pull-down m7GTP n’est pas lié au GTP en général mais spécifiquement à la forme du GTP qui est présente dans la coiffe des ARNm. Cela montre la spécificité de liaison. On constate que METTL16 ne se fixe à la coiffe, mais eIF4E2 et eIF4E si. Cependant, en absence de METTL16 dans la cellule, eIF4E2 est plus fixé à la coiffe qu’en sa présence et c’est l’inverse pour eIF4E. 13.4 : METTL16 va très probablement stimuler la traduction car son absence facilite la fixation d’un inhibiteur de la traduction sur la coiffe et rend plus difficile la fixation d’un activateur de la traduction sur cette coiffe.
14.1 : On utilise un promoteur d’un gène exprimé de manière généralisée dans toutes les cellules de la drosophile pour que la GFP soit exprimée de manière ubiquitaire et que toute inhibition localisée de sa production soit facilement repérable. 14.2 : On constate que de larges zones du disque imaginal n’expriment pas le GFP lorsque les séquences cibles du microARN Bantam se trouvent dans le 3’UTR de l’ARNm de la GFP, contrairement à la situation contrôle où la GFP est exprimée quasiment partout. On en déduit que le microARN Bantam est exprimé et inhibe la traduction de ces cibles dans les régions devenues non fluorescentes chez la drosophile transgénique de droite.
15.1 : La fraction 40S correspond à la petite sous-unité des ribosomes des Eucaryotes, la fraction 60S à la grande sous-unité et la fraction 80S au ribosome entier (petite et grande sous-unités associées). 15.2 : On observe que les quantités de sous-unités 40S, 60S et 80S sont plus faibles chez les drosophiles clu que chez les drosophiles sauvages. Il y a donc un défaut de formation de ribosomes chez les mutants dès l’étape de la formation des petites et des grandes sous-unités. Alternativement, il pourrait s’agir d’une dégradation accélérée des sous-unités ribosomiques. 15.3 : Il faut analyser les ratios 18S/ETS1 et 28S/ETS1 pour normaliser l’expression des gènes ribosomiques avec l’expression générale. On constate qu’il n’y a aucune différence d’expression pour l’ARNr 18S entre le sauvage et le mutant et une légère augmentation pour l’expression de l’ARNr 28S chez le mutant. Le déficit de sous-unités ribosomiques chez le mutant ne provient donc pas d’une défaut de transcription des gènes codant les ARNr 18S et 28S ou de leur plus grande dégradation. 15.4 : Une coloration rouge Ponceau permet de mettre en évidence toutes les protéines qui ont été transférées du gel de polyacrylamide vers la membrane du western-blot. Cela permet de vérifier si des quantités équivalentes de protéines ont été ajoutées dans les différents puits du gel et si le transfert a été uniforme. On observe ici qu’il y a dû y avoir un défaut de transfert du côté droit en haut du gel. 15.5 : Les deux puits WT et clud87 présentent le même niveau de détection de Tom20 et une coloration rouge Ponceau similaire. On peut considérer que la même quantité de protéines a été introduite dans le gel puis transférée sur la membrane. On constate que la protéine Clu est complètement absente chez le mutant clud87 qui est donc un mutant de perte-de-fonction total. La protéine ribosomale RpS15Aa est correctement exprimée chez le mutant. En revanche, la protéine ribosomale RpL9 est légèrement moins exprimée et surtout il y a une forte baisse d’expression de la protéine ribosomale RpS11. Cela peut expliquer en partie la baisse de la quantité des sous-unités des ribosomes chez le mutant.
Retour à la page sur le contrôle de la transcription.
Retour à la page sur le contrôle de la traduction.